Gerelateerd artikel
Hoe Resultaten Te Valideren: ChIP-Seq Data Analyse Pipeline Uitgelegd
2026-02-27ChIP-Seq Data Analysis Pipeline validatie is de stap die pieken omzet in bewijs, niet alleen in afbeeldingen. Bij Longlight Technology ondersteunen we ChIP-seq-projecten van voorbeeld tot rapport, en we zien één duidelijke regel: als je in de juiste volgorde valideert, worden je conclusies stabiel, verklaarbaar en makkelijker te publiceren.
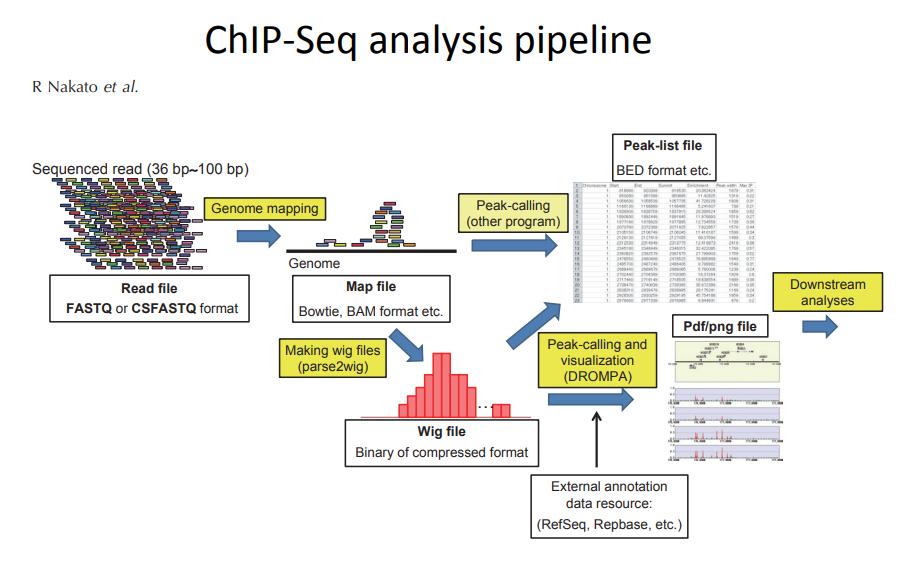
Een beginnersgids voor ChIP-Seq data-analyse | Door Sezer Islambey | Medium
1) Begrijpen wat ChIP-seq bewijst, eenen Wat Het Niet Doet
ChIP-seq begint met een eenvoudig wetenschappelijk doel: meten hoe eiwitten interageren met DNA in echte biologische monsters. In de praktijk helpt het je in kaart te brengen waar transcriptiefactoren, RNA-polymerase II of histonmodificaties over het genoom zijn verrijkt. Een goed opgebouwde ChIP-Seq Data Analysis Pipeline kan vragen ondersteunen zoals de aanwezigheid van eiwitten op verschillende genomische locaties, het bindingsgedrag van transcriptiefactoren en hoe histonmarkeringen zich verhouden tot genexpressie.
Validatie is belangrijk omdat ChIP-seq een keten van gekoppelde stappen is. Als één schakel zwak is—antistofspecificiteit, chromatinekwaliteit, bibliotheekcomplexiteit of achtergrondcontrole—kunnen je uiteindelijke pieken overtuigend lijken maar nog steeds onbetrouwbaar zijn. Een beginnersvriendelijke manier om over validatie na te denken is deze: je probeert niet "pieken te krijgen." Je probeert aan te tonen dat de pieken onder dezelfde omstandigheden opnieuw zouden verschijnen, en dat ze overeenkomen met de biologie die je verwacht.
✓ ChIP-seq meet verrijking, niet absolute bindingsaantallen
✓ Goede resultaten vereisen besturing en herhaalbaarheid, niet alleen sequencingdiepte
✓ Validatie moet worden gepland voordat het experiment begint, niet nadat pieken zijn aangekondigd
2) Validatie inbouwen in thij werkstroom vanuit the Eerste Voorbeeld
Veel teams richten zich alleen op validatie in de bio-informaticafase. Dat is vaak te laat. De meest efficiënte validatiemethode is om het vanaf het begin onderdeel van het serviceproces te maken, omdat vroege controle laat herwerken voorkomt.
Besteed de hele pijplijn uit: je levert vaste cellen of ingevroren weefselmonsters; Longlight Technology levert voorbereiding, chromatineverwerking, bibliotheekconstructie, sequencing en analyse. Het voordeel is niet alleen gemak. Het vermindert het overdrachtsrisico en zorgt ervoor dat kwaliteitscontroles consistent zijn over alle stappen, waardoor de uiteindelijke output van de ChIP-Seq Data Analysis Pipeline gemakkelijker te vertrouwen is.
Wanneer de invoer van het monster beperkt is, wordt validatie nog belangrijker. Ons geoptimaliseerde proces is geschikt voor kleine steekproefgroottes, wat onderzoekers helpt om verder te gaan wanneer materiaal kostbaar is. De praktische waarde voor klanten is eenvoudig: minder monsterverspilling, minder trial-and-error herhalingen en duidelijkere beslissingen eerder in het project.
✓ Eén proceseigenaar vermindert variatie tussen stappen
✓ Standaard controlepunten voorkomen "onzichtbare storingen"
✓ Kleine monsterparaatheid beschermt zeldzame weefsels en projecten met lage opbrengst
3) Valideer de datakwaliteit voordat je een piek vertrouwt
Een sterke ChIP-Seq Data Analysis Pipeline begint met kwaliteitscontrole die één vraag beantwoordt: is uw dataset in staat om een echt signaal boven de achtergrond te produceren?
Begin met het beoordelen van de kwaliteit van data buiten de machine en het basisgedrag van de bibliotheek. Als de input DNA of de ChIP-bibliotheek abnormale leeskwaliteit, sterke adapteraanwezigheid of extreme duplicatie vertoont, kan piekaanroepen ruis versterken. Goede bevestiging jaagt niet op perfectie. Het zoekt naar consistentie tussen samples en duidelijke scheiding tussen ChIP en controle.
Bevestig vervolgens het alignementgedrag en de filterregels. De mappingsnelheid en het aandeel bruikbare reads zouden niet enorm moeten schommelen tussen replicaten. Als één replicate zich anders gedraagt, negeer die dan niet. Behandel het als een signaal dat er iets veranderd is in het experiment of de verwerking van monsters.
Voor beginners is vergelijken de meest praktische gewoonte. Vergelijk:
• ChIP versus Input
• Repliceren A versus Repliceren B
• Behandeling versus controle onder dezelfde verwerkingsregels
Hier wordt "strikte kwaliteitscontrole in elke link" echte waarde. Wanneer QC elke keer op dezelfde manier wordt toegepast, kun je snel de ware uitschieter identificeren en voorkomen dat je conclusies trekt op basis van een onstabiele steekproef.
✓ Valideer de dataset voordat piekoproepen later tijd bespaart
✓ Consistente filtering voorkomt kunstmatige verschillen
✓ Uitschieters moeten worden gedocumenteerd, niet verborgen
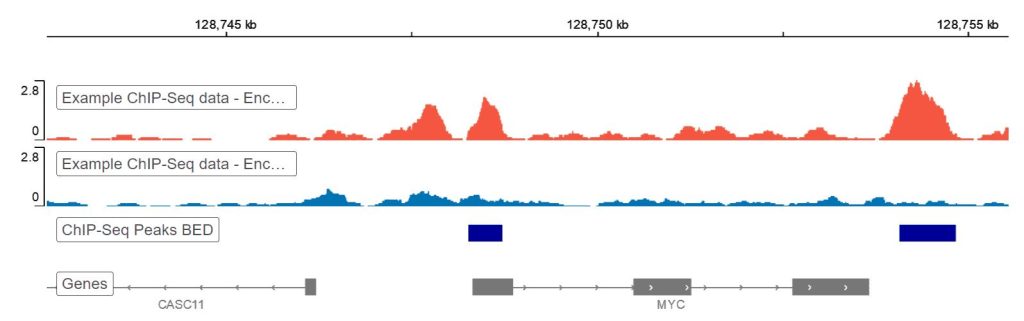
ChIP-Seq Analyse Tutorial - Basepair
4) Valideer pieken met regelingen eennd Doel-geschikte Logica
Peak calling is niet één enkele knop. Het is een beslissingssysteem. Een ChIP-seq-doel kan een smalbindende transcriptiefactor zijn of een bredere histonmodificatie, en je validatiemethode moet overeenkomen met de biologie.
Besturing is de eerste beproefde laag. Input-DNA helpt bij het modelleren van achtergrondsignalen en vermindert valse verrijking door open chromatine, repetitieve gebieden of sequencing-bias. Als pieksets drastisch veranderen wanneer de besturing wordt toegepast, kun je mogelijk pieken zien die op de achtergrond worden aangestuurd in plaats van echte binding.
Vervolgens valideer je de piekvorm en verrijkingslogica. Transcriptiefactorpieken verschijnen vaak scherp en gelokaliseerd, terwijl sommige histonmarkeringen bredere gebieden vormen. Een mismatch tussen de verwachte signaalvorm en de waargenomen sporen is een reden om upstream experimentele omstandigheden opnieuw te controleren, niet alleen software-drempels aan te passen.
Longlight ondersteunt ook de analyse van specifieke genen of regio's op basis van het onderzoeksdoel van de klant. Voor veel projecten is dit de meest uitvoerbare validatiestap. Als je hypothese zich richt op een gedefinieerd pad of een doelgenomisch gebied, moet validatie gerichte beoordeling van die loci bevatten, niet alleen een globale piektelling.
✓ Gebruik Input om verrijking van achtergrond te scheiden
✓ Match topstrategie met TF versus histoongedrag
✓ Valideer belangrijke genen of regio's die belangrijk zijn voor je onderzoeksvraag
5) Valideer reproduceerbaarheid vóór een differentiële claim
De meest overtuigende validatie is reproduceerbaarheid. Als replicaten niet overeenkomen, kunnen "differentiële pieken" een verhaal worden over ruis in plaats van biologie.
Een praktische ChIP-Seq Data Analysis Pipeline moet replicatovereenkomst op twee niveaus controleren: genoombrede signaalgelijkheid en piekoverlapstabiliteit. Je kunt ook onderzoeken of toppieken nog steeds bovenaan staan bij replicaten. Als slechts één replica het resultaat veroorzaakt, is je conclusie fragiel.
Voor beginners helpt het om een eenvoudige standaard te stellen: je moet kunnen uitleggen waarom een piek als betrouwbaar wordt beschouwd. Die verklaring omvat meestal consistente aanwezigheid tussen replicates, sterkere verrijking dan controle, en een signaalprofiel dat past bij het doeltype.
Hier helpt strikte kwaliteitscontrole klanten ook direct. Sterke kwaliteitscontrole vermindert herhaalde experimenten en vergroot de kans dat je eindrapport een publiceerbare conclusie ondersteunt in plaats van alleen een interne observatie.
✓ Replicate-overeenkomst is een vereiste, geen bonus
✓ Differentiaalanalyse moet gebaseerd zijn op stabiele pieken
✓ "Verklaarbare toppen" zijn veiliger dan "meer toppen"
6) Validatie omzetten in een Rapport dat je kunt gebruiken eenen delen
Validatie is alleen waardevol als het een duidelijk rapport wordt waarop anderen kunnen vertrouwen. Een volledige output moet ruwe datalevering, gestandaardiseerde QC-samenvattingen, peak call-instellingen en de logica die wordt gebruikt om reproduceerbaarheid te bevestigen bevatten. Het moet ook resultaten vertalen naar biologische interpretatie: piekannotatie, beoordeling van doelgebieden en betekenisvolle voorbeelden die aansluiten bij je hypothese.
Longlight Technology ondersteunt moderne genomica met geïntegreerde oplossingen—NGS-gerelateerde instrumenten, reagentia-verbruiksartikelen en laboratoriumworkflows die worden gebruikt in academische, klinische en industriële omgevingen. In de praktijk betekent dit dat onderzoekers de experimentele uitvoering kunnen afstemmen op downstream analysestandaarden, in plaats van ze als aparte werelden te behandelen. We bieden ook veelgebruikte verbruiksmaterialen en kits zoals qubitbuizen, nucleïnezuurextractiekits en bibliotheekvoorbereidingskits, die stabiele workflows over meerdere projecttypen ondersteunen.
CTA (Call-To-Action): Als u een ChIP-seq-project wilt dat stapsgewijs wordt gevalideerd — van monsterverwerking tot een volledig datarapport — neem dan contact op met Longlight Technology voor een technisch consult en een gratis offerte. Wij leveren een speciaal ontwikkelde validatiechecklist voor uw doelcategorie en zorgen ervoor dat controles en rapportages vooraf worden afgesproken voor een soepele downstream workflow.
• Vraag een geïntegreerd ChIP-seq-plan aan dat is afgestemd op uw onderzoeksdoelen
• Nominatie van prioritaire genen/regio's voor gerichte analyse
• Volledige rapporten met ruwe gegevens en validatiesamenvattingen verkrijgen